
Avanços na Detecção Rápida de Salmonella em Aves: Métodos Inovadores para Combater a Resistência e Melhorar a Segurança Alimentar
O que é a Salmonella enterica?
A Salmonella enterica é uma bactéria que pode infectar tanto animais quanto seres humanos. Ela é uma das principais causas de intoxicação alimentar, especialmente quando comemos alimentos contaminados, como carne de frango e ovos. Duas variantes específicas dessa bactéria, chamadas Typhimurium e Heidelberg, são comuns em aves e podem ser perigosas para os seres humanos, causando doenças graves. Tradicionalmente, identificar essas variantes era um processo demorado, e os testes nem sempre forneciam resultados claros, já que as bactérias podem ter características semelhantes.
A salmonelose nas aves provoca grandes perdas econômicas para a indústria de aves e é uma doença que também pode afetar os humanos, por isso é chamada de zoonose. Além disso, algumas cepas de Salmonella se tornaram resistentes aos antibióticos, tornando o tratamento mais difícil e exigindo um monitoramento constante para prevenir infecções.
Metodologia I
Os pesquisadores desenvolveram um novo teste chamado SHTAmp, que é uma técnica rápida de PCR em tempo real (uma forma de amplificar e detectar o DNA das bactérias). Eles aplicaram esse método em 147 amostras de Salmonella de aves no Brasil, e também testaram 34 amostras de aves após um processo inicial de preparo.
Resultados Metodologia I
O SHTAmp conseguiu identificar corretamente 21 amostras de S. Typhimurium e 57 de S. Heidelberg. Além disso, foi capaz de detectar variantes dessas bactérias, chamadas de monofásicas, ou incompletas, que são mais difíceis de identificar com métodos tradicionais. Isso mostrou que o método pode ser utilizado diretamente nas amostras de aves, sem a necessidade de etapas complexas.
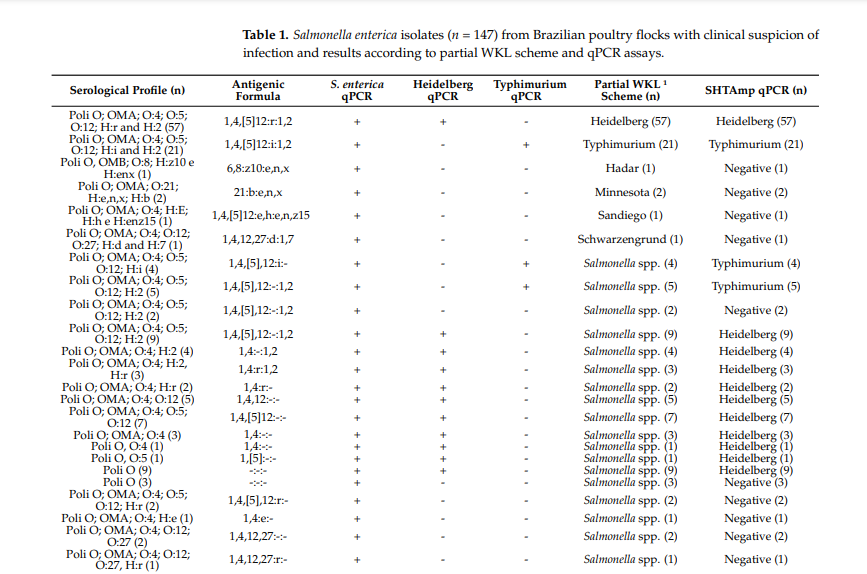
Tabela 1. Comparação de resultados gerados por metodologia tradicional e método de SHTAmp qPCR mostrando maior eficácia para identificar variedades que por metodologia tradicional não foi possível
Metodologia II
Outro estudo foi realizado no Egito com 450 amostras de frangos doentes. As amostras foram testadas para ver se continham Salmonella e se as bactérias tinham resistência a antibióticos. Além disso, os cientistas verificaram a presença de genes que tornam as bactérias mais perigosas, como genes de resistência a antibióticos e genes de virulência (que ajudam as bactérias a causar doenças).
Resultados Metodologia II
Desses 450 testes, 9,3% das amostras foram positivas para Salmonella, com uma prevalência maior nos swabs (amostras) da cloaca (parte do corpo das aves). As duas variedades de Salmonella identificadas foram S. Enteritidis e S. Typhimurium. Além disso, os cientistas descobriram que essas bactérias eram resistentes a vários antibióticos, como ampicilina e amoxicilina, e possuíam genes que indicam um alto poder de causar doenças.
Conclusão das Metodologias
- Metodologia I: O teste SHTAmp é um método rápido e preciso para detectar as variedades de Salmonella que afetam as aves, incluindo suas variantes mais difíceis de identificar. Esse método pode melhorar a segurança alimentar, facilitando a detecção de Salmonella nas aves e ajudando a controlar a disseminação da bactéria, o que é importante para a saúde pública.
- Metodologia II: O estudo no Egito revela que existem cepas de Salmonella resistentes a vários antibióticos nas aves, o que é preocupante. Esses resultados ressaltam a necessidade de melhorar as práticas de segurança na criação de aves e usar antibióticos com mais cautela para evitar o crescimento de bactérias resistentes.
Conclusão
Os avanços nos métodos de detecção da Salmonella podem melhorar a vigilância e controle da bactéria, prevenindo surtos de infecções. É essencial que a indústria de aves adote práticas de biossegurança e controle rigorosas para garantir que esses patógenos não se espalhem e causem danos à saúde pública.
Referência:
Mathias, J. B., Souza, M. N., Kipper, D., Fonseca, A. S. K., Lunge, V. R., & Ikuta, N. (2024). Rapid DNA detection of Salmonella enterica Typhimurium and Heidelberg from poultry samples. Poultry, 3(1), 47–56. https://doi.org/10.3390/poultry3010005



